染色质可及性-转座酶易接近染色质测序(ATAC-Seq)
真核生物的DNA并不是裸露的,而是被包装成核小体形成串珠状结构并进一步被折叠、包装。而基因的转录,需要将这种高级结构解开,使DNA成为可以使各种转录机器与其结合的裸露状态,即形成开放染色质区域。如何鉴定开放染色质区域呢?传统的方法主要是借助和DNase-Seq、MNase-Seq及ChIP-seq。但这些方法需要的起始细胞量较大,对于少量样本和珍稀样本可行性不高。ATAC-Seq是一种新型的研究开放染色质的技术,利用Tn5转座酶进入并切割裸露的DNA,并同时连接上特异性的测序接头。因为切割和加接头一步完成,因此该技术可大大降低所需细胞起始量。
技术优势:
实验策略:

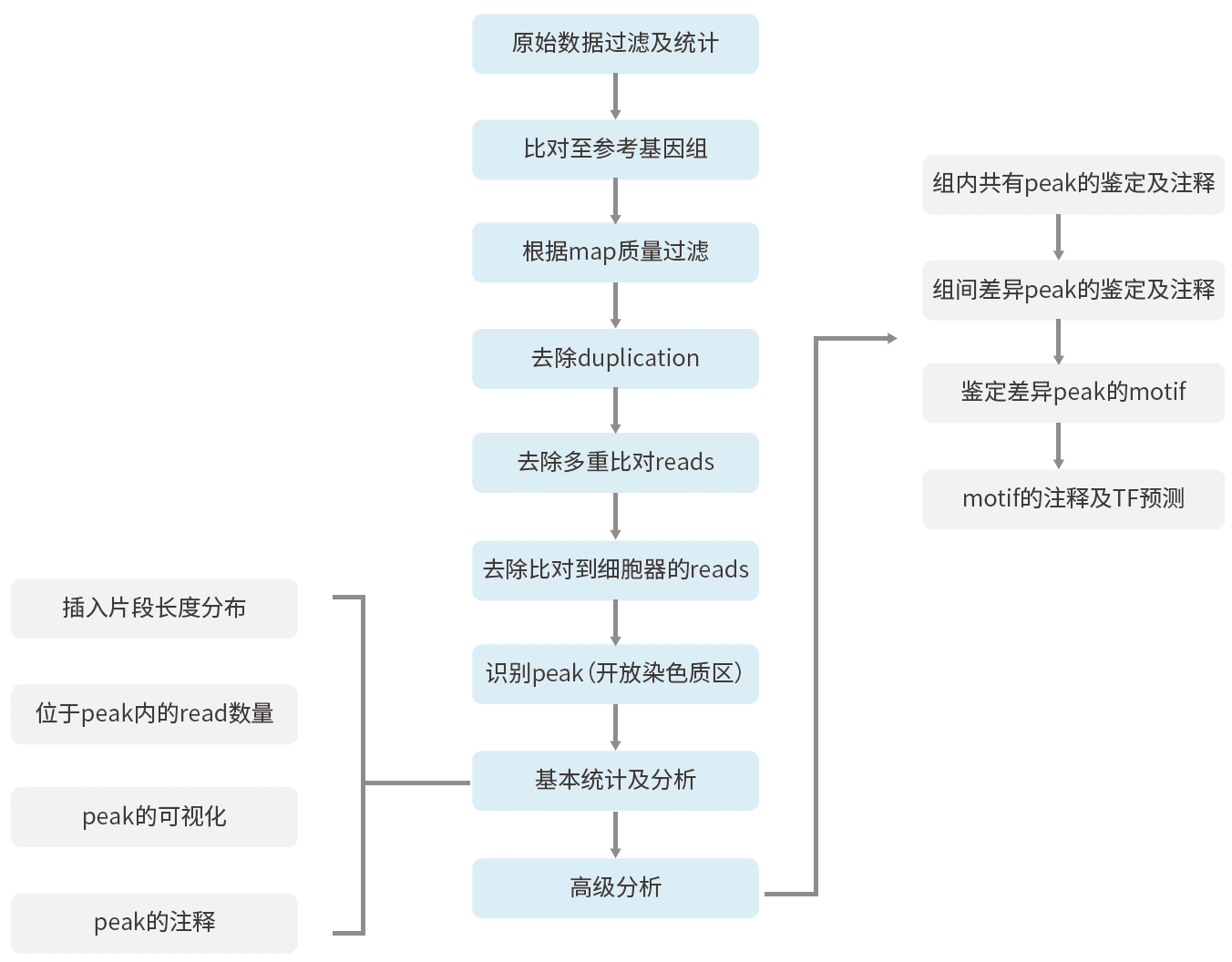
信息分析:
样本要求:

研究案例:
Wang J, Zibetti C, Shang P, et al. ATAC-Seq analysis reveals a widespread decrease of chromatin accessibility in age-related macular degeneration[J]. Nature Communications, 2018, 9(1).
1、背景:
年龄相关性黄斑变性(AMD)是导致老年人视力丧失的主要因素,大多发生于45岁以上,其患病率随年龄增长而增高。目前AMD进程中表观遗传的改变尚不清楚。本文利用ATAC-Seq对AMD患者视网膜(retina)及视网膜色素上皮细胞(RPE)进行染色质易近性进行了研究。
2、方法:
利用ATAC-Seq技术鉴定AMD及正常组织的retina及RPE的开放染色质区域。另外,结合RNA-Seq技术对开放染色质区域与基因表达的关系进行分析。
3、结论:
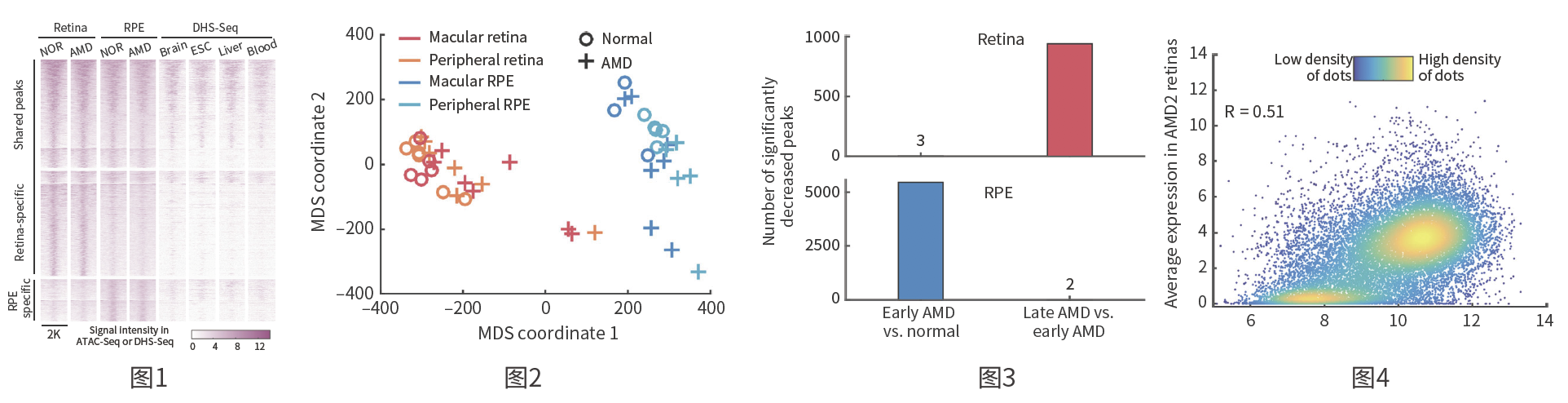
将鉴定出的peak(开放染色质区域)分类得到retina特异、RPE特异及两者共有的peak,与不同组织比较(DNase-Seq数据),发现两者共有的peak大部分是组织特异的,retina及RPE特异的peak大多是组织特异的(下图1)。利用peak将样本分类,发现retina和RPE明显分开,正常组织和AMD也有分离的趋势(下图2)。
分别鉴定retina和RPE AMD早期vs正常组织以及AMD晚期vs AMD早期的差异开放染色质区域(AMD),表明retina染色质易近性主要在AMD早期到AMD晚期出现下降,而RPE染色质易近性主要在正常组织到AMD早期出现下降(下图3)。结合转录组分析表明,ATAC-Seq peak强度和基因表达呈现较强相关性,相关系数为0.51(下图4)。
参考文献:
① DOI:10.1038/s41467-018-03856-y
点击下方阅读全文
表观组学|ATAC-Seq
