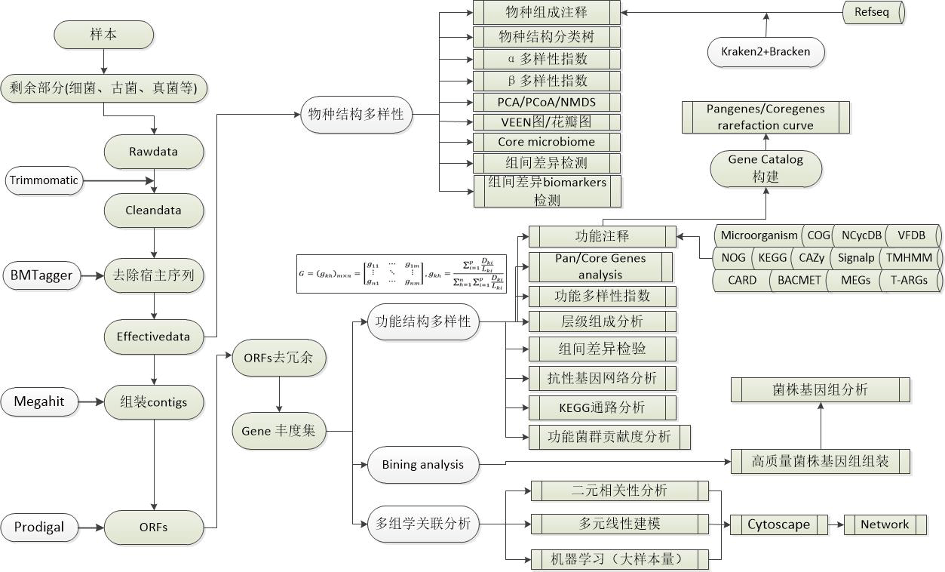
宏基因组测序
由于扩增子测序技术关注的是目标基因的若干区域,因此其分辨率有限,一般认为较为准确的分类水平到属级别。虽然扩增子测序也可以通过数据库映射预测群落可能的功能网络,但是微生物遗传片段交流比较频繁,功能基因的横向转移也较为普遍,依托于有限菌株建立的功能映射无法尽可能的还原群落的真实功能网络。全宏基因组测序技术直接对提取的全宏基因组DNA建立随机小片段文库,能够获取更多的序列信息。通过组装、ORFs预测与注释,可以大大提高分类水平部分至菌株级别,并通过各种大型公共数据库进行相应功能注释,尽可能真实的获取群落功能网络信息。高精度的分析结果也使相关动物验证实验更加具备可行性。
技术优势
实验策略

信息分析
送样要求

案例研究
膳食纤维通过选择性重塑肠道菌群改善Ⅱ型糖尿病
Zhao L, Zhang F, Ding X, et al. Gut bacteria selectively promoted by dietary filbers alleviate type 2 diabetesJ. Science.2018,359(6380):1151-1156
1、背景
肠道菌群作为人类的“第二基因组”,其稳态与人体生理代谢水平、免疫系统的正常运转有着密切的关系。型糖尿病又名非胰岛素依赖型糖尿病,特点是人体自身能够产生胰岛素,但细胞无法对其作出反应,因此患者的血糖调控是种失衡状态。由于其发病机制非常复杂及伴随多种并发症进而成为了影响人类健康的杀手之一。近年来的研究表明,肠道菌群降解纤维多糖产生的短链脂肪酸可显著改善l1型糖尿病人的治疗效果。但是肠道内能产生短链脂肪酸的微生物种类繁复,需要找出哪些微生物对疾病的改善起到至关重要的作用。
2、方法
利用宏基因组学与靶向代谢组学技术,发现高复合膳食纤维选择性富集出的产短链脂肪酸(SCFAs)的肠道细菌可显著改善2型糖尿病。
3、结论
研究表明额外增加大量结构多样化的膳食纤维,可以快速显著地改善II型糖尿病人的各项临床指标。该研究发现干预前后的样本中菌群CAZy基因集谱存在显著差异,干预模式也对碳水化合物代谢能力产生了一定影响,具体体现在膳食纤维代谢产物的含量差异上。基于深度测序的宏基因组数据组装出154个高质量细菌基因组草图,并在众多产SCFAS菌种中筛选出15株显著富集菌株,这些菌株均为在高腾食纤维干预下II型糖尿病患者肠道中有活性的主要短链脂肪酸产生者。通过15个显著富集菌株与肠道微生态系统中其他成员间的相关性分析,发现它们具备更强的生态竞争力。它们通过发酵膳食纤维产生短链脂肪酸,维持适于自身生长的健康肠道环境,从而降低有害菌的生长,保持宿主的健康。最终利用动物实验验证目的菌株对II型糖尿病的良好调控作用。
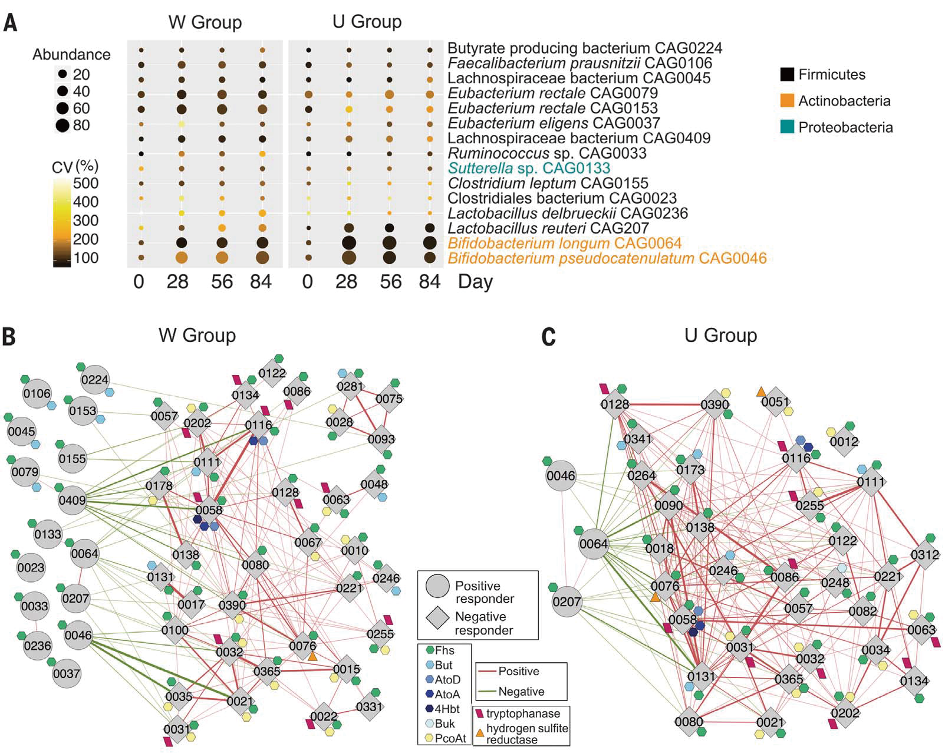
15株显著富集产SCFAs菌株以及其与生态系统中其他成员关联网络
参考文献:
① DOI:10.1126/science.aao5774
